QIEP
RA95.0: retro-aldolasa sobre bastida TIM
Grup G · Química i Enginyeria de Proteïnes 2025-2026
Seqüència problema
Aquesta és la cadena aminoacídica analitzada. La identificació de la proteïna o del constructe es fa a partir d’aquesta seqüència, i totes les correspondències amb UniProt, PDB, CATH/ECOD o AlphaFold s’han d’interpretar en relació amb aquesta numeració.
>JC G | 2025-2026 | seqüència problema
MPRYLKGWLEDVVQLSLRRPSVRASRQRPIISLNERILEFNKRNITAIIAVYERKSPSGLDVERDPIEYAKFMERYAVGL
SITTEEKYFNGSYETLRKIASSVSIPILMSDFIVKESQIDDAYNLGADTVLLIVKILTERELESLLEYARSYGMEPLILI
NDENDLDIALRIGARFIGIMSRDFETGEINKENQRKLISMIPSNVVKVAKLGISERNEIEELRKLGVNAFLISSSLMRNP
EKIKELIEGSLEHHHHHH
Seqüència extreta del fitxer FASTA oficial de selecció 2025-2026. Longitud: 258 aminoàcids.
Identificació i estructura de referència
La seqüència anterior defineix la molècula analitzada i evita confondre el nom abreujat del sistema amb una proteïna natural completa. La cerca a RCSB PDB proporciona com a estructura de referència 4A29 entitat 1, amb cobertura de la seqüència 100.0%, identitat 100.0% i resolució 1.1 Å. La longitud de la seqüència analitzada és de 258 aminoàcids. Registre UniProt candidat Q06121 (indole-3-glicerol fosfat sintasa), vinculat a l’entitat PDB recomanada. Gen: trpC.
| Camp | Valor |
|---|---|
| UniProt / gen | Q06121; gen: trpC |
| EC / BRENDA | 4.1.1.48. Consulteu BRENDA a partir del número EC indicat. |
| Estructura principal | 4A29 entitat 1; difracció de raigs X, 1.1 Å |
| Cobertura i identitat | 100.0% de cobertura; 100.0% d’identitat |
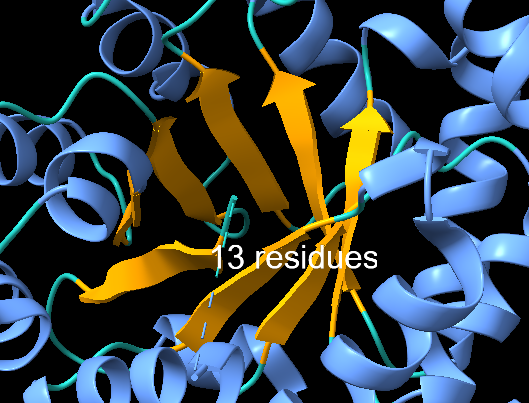
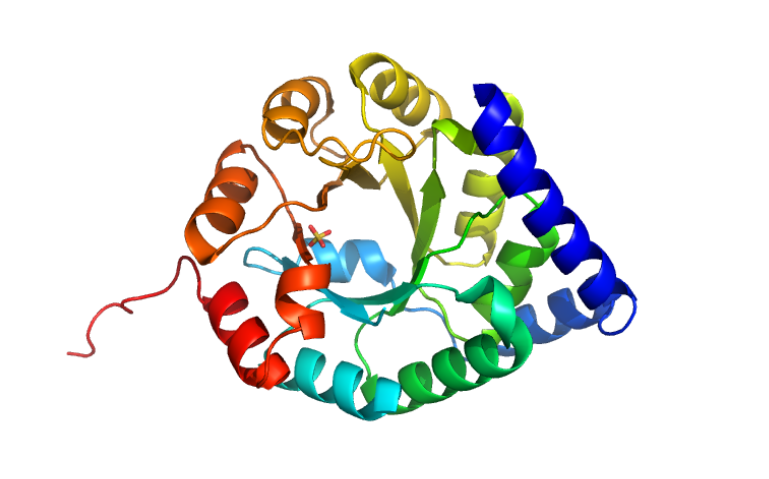
| Dominis i plegament | bastida de barril TIM/aldolasa de classe I, CATH 3.20.20.70, usada com a suport de la retro-aldolasa RA95.0 |
| Estructura secundària i lectura ChimeraX | làmina β: 1, hèlix: 12, regions no assignades: 1; exemples: làmina β 48-52, 229-232, 206-211, 176-179, 157-160, 129-133, 107-110, 79-83, 48-52; hèlix 6-18; hèlix 32-43; hèlix 65-74; hèlix 92-101; hèlix 115-126; hèlix 135-137; hèlix 138-152 |
| Lligands o cofactors a revisar | No s’han identificat lligands no polimèrics en aquesta entrada PDB; els pèptids, cadenes associades o socis polimèrics s’han de revisar per separat. |
| Trets de constructe | etiqueta d’histidines 253-258 (HHHHHH) |
Funcionalment, RA95.0 és una retro-aldolasa dissenyada sobre una bastida TIM. La funció natural IGPS/trpC i l’EC 4.1.1.48 s’han de presentar com a context estructural o evolutiu, no com a funció directa del constructe. 4A29 cobreix tota la seqüència assignada amb identitat completa. 3QJA, una IGPS nativa d’alta resolució, és útil com a comparació de bastida però no substitueix 4A29 per explicar identitat, funció o residus del constructe.
| Paràmetre | Valor |
|---|---|
| Proteïna o constructe | RA95.0 |
| Estructura de referència | 4A29 |
| Longitud | 258 aa |
| Trets rellevants | His 253-258; sense Cys |
Arquitectura molecular
RA95.0 manté el patró de barril TIM: làmines β al centre i hèlixs envoltants. Aquesta disposició crea una cavitat modulable on canvis puntuals de seqüència poden generar una activitat química nova.
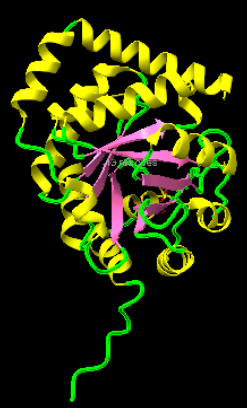
Lloc funcional i mecanisme
La funció del constructe és retro-aldolasa dissenyada. IGPS/trpC i EC 4.1.1.48 són context de la bastida natural; la discussió funcional de RA95.0 se centra en la catàlisi retro-aldòlica.
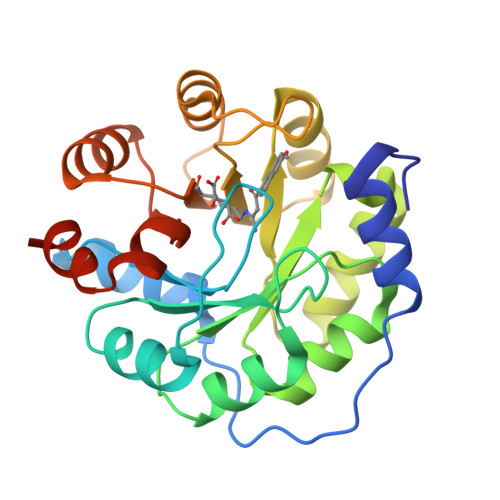
La interpretació estructural i funcional d’aquest sistema es pot situar en el context de la literatura experimental corresponent (Giger et al., 2013).
Modificacions i variants
RA95.0 és un constructe dissenyat; no s’hi han d’importar variants o modificacions posttraduccionals de la IGPS natural sense alineament. Les posicions determinants són les mutacions que creen la cavitat retro-aldolasa i la geometria del centre catalític al PDB 4A29.
Relació seqüència-estructura-funció
Els residus catalítics d’IGPS no es transfereixen automàticament a RA95.0. La comparació útil és un remapeig 3QJA-4A29 que identifiqui posicions equivalents i mutacions responsables de la nova reactivitat.

Referències
- Giger, L. et al. (2013). Evolution of a designed retro-aldolase leads to complete active site remodeling. Nature Chemical Biology. doi: 10.1038/nchembio.1276. La família RA95 prové del disseny computacional de retro-aldolases: Jiang, L. et al. (2008), doi: 10.1126/science.1152692.