QIEP
Pràctica 1; Química i Enginyeria de Proteïnes, UVic-UCC 22-23
QiEP: Pràctica 1. Proteïnes que digereixen proteïnes
L’exercici consisteix a explorar l’estructura de sis proteïnes, una per a cada grup de la classe, de les quals ens donen les seqüències:
>A
MDFSRNLYDIGEQLDSEDLASLKFLSLDYIPQRKQEPIKDALMLFQRLQEKRMLEESNLSFLKELLFRINRLDLLITYLNTRKEEMERELQTPGRAQISAYRVMLYQISEEVSRSELRSFKFLLQEEISKCKLDDDMNLLDIFIEMEKRVILGEGKLDILKRVCAQINKSLLKIINDYEEFSKERSSSLEGSPDEFSNGEELCGVMTISDSPREQDSESQTLDKVYQMKSKPRGYCLIINNHNFAKAREKVPKLHSIRDRNGTHLDAGALTTTFEELHFEIKPHDDCTVEQIYEILKIYQLMDHSNMDCFICCILSHGDKGIIYGTDGQEAPIYELTSQFTGLKCPSLAGKPKVFFIQACQGDNYQKGIPVETDSEEQPYLEMDLSSPQTRYIPDEADFLLGMATVNNCVSYRNPAEGTWYIQSLCQSLRERCPRGDDILTILTEVNYEVSNKDDKKNMGKQMPQPTFTLRKKLVFPSD
>B
MSDMEKPWKEEEKREVLAGHARRQAPQAVDKGPVTGDQRISVTVVLRRQRGDELEAHVERQAALAPHARVHLEREAFAASHGASLDDFAEIRKFAEAHGLTLDRAHVAAGTAVLSGPVDAVNQAFGVELRHFDHPDGSYRSYVGDVRVPASIAPLIEAVLGLDTRPVARPHFRLRRRAEGEFEARSQSAAPTAYTPLDVAQAYQFPEGLDGQGQCIAIIELGGGYDETSLAQYFASLGVSAPQVVSVSVDGATNQPTGDPNGPDGEVELDIEVAGALAPGAKIAVYFAPNTDAGFLNAITTAVHDPTHKPSIVSISWGGPEDSWAPASIAAMNRAFLDAAALGVTVLAAAGDSGSTDGEQDGLYHVDFPAASPYVLACGGTRLVASAGRIERETVWNDGPDGGSTGGGVSRIFPLPSWQERANVPPSANPGAGSGRGVPDVAGNADPATGYEVVIDGETTVIGGTAAVAPLFAALVARINQKLGKPVGYLNPTLYQLPPEVFHDITEGNNDIANRARIYQAGPGWDPCTGLGSPIGIRLLQALLPSASQAQP
>C
MLGITVLAALLACASSCGVPSFPPNLSARVVGGEDARPHSWPWQISLQYLKNDTWRHTCGGTLIASNFVLTAAHCISNTRTYRVAVGKNNLEVEDEEGSLFVGVDTIHVHKRWNALLLRNDIALIKLAEHVELSDTIQVACLPEKDSLLPKDYPCYVTGWGRLWTNGPIADKLQQGLQPVVDHATCSRIDWWGFRVKKTMVCAGGDGVISACNGDSGGPLNCQLENGSWEVFGIVSFGSRRGCNTRKKPVVYTRVSAYIDWINEKMQL
>D
MAQALPWLLLWMGAGVLPAHGTQHGIRLPLRSGLGGAPLGLRLPRETDEEPEEPGRRGSFVEMVDNLRGKSGQGYYVEMTVGSPPQTLNILVDTGSSNFAVGAAPHPFLHRYYQRQLSSTYRDLRKGVYVPYTQGKWEGELGTDLVSIPHGPNVTVRANIAAITESDKFFINGSNWEGILGLAYAEIARPDDSLEPFFDSLVKQTHVPNLFSLQLCGAGFPLNQSEVLASVGGSMIIGGIDHSLYTGSLWYTPIRREWYYEVIIVRVEINGQDLKMDCKEYNYDKSIVDSGTTNLRLPKKVFEAAVKSIKAASSTEKFPDGFWLGEQLVCWQAGTTPWNIFPVISLYLMGEVTNQSFRITILPQQYLRPVEDVATSQDDCYKFAISQSSTGTVMGAVIMEGFYVVFDRARKRIGFAVSACHVHDEFRTAAVEGPFVTLDMEDCGYNIPQTDESTLMTIAYVMAAICALFMLPLCLMVCQWRCLRCLRQQHDDFADDISLLK
>E
MTMEKGMSSGEGLPSRSSQVSAGKITAKELETKQSYKEKRGGFVLVHAGAGYHSESKAKEYKHVCKRACQKAIEKLQAGALATDAVTAALVELEDSPFTNAGMGSNLNLLGEIECDASIMDGKSLNFGAVGALSGIKNPVSVANRLLCEGQKGKLSAGRIPPCFLVGEGAYRWAVDHGIPSCPPNIMTTRFSLAAFKRNKRKLELAERVDTDFMQLKKRRQSSEKENDSGTLDTVGAVVVDHEGNVAAAVSSGGLALKHPGRVGQAALYGCGCWAENTGAHNPYSTAVSTSGCGEHLVRTILARECSHALQAEDAHQALLETMQNKFISSPFLASEDGVLGGVIVLRSCRCSAEPDSSQNKQTLLVEFLWSHTTESMCVGYMSAQDGKAKTHISRLPPGAVAGQSVAIEGGVCRLESPVN
>F
MRGLLVLSVLLGAVFGKEDFVGHQVLRISVADEAQVQKVKELEDLEHLQLDFWRGPAHPGSPIDVRVPFPSIQAVKIFLESHGISYETMIEDVQSLLDEEQEQMFAFRSRARSTDTFNYATYHTLEEIYDFLDLLVAENPHLVSKIQIGNTYEGRPIYVLKFSTGGSKRPAIWIDTGIHSREWVTQASGVWFAKKITQDYGQDAAFTAILDTLDIFLEIVTNPDGFAFTHSTNRMWRKTRSHTAGSLCIGVDPNRNWDAGFGLSGASSNPCSETYHGKFANSEVEVKSIVDFVKDHGNIKAFISIHSYSQLLMYPYGYKTEPVPDQDELDQLSKAAVTALASLYGTKFNYGSIIKAIYQASGSTIDWTYSQGIKYSFTFELRDTGRYGFLLPASQIIPTAKETWLALLTIMEHTLNHPY
Usarem eines com:
- Chimera per a la visualització de proteïnes.
- UNIPROT per a obtenir informació sobre una proteïna determinada.
- PDB per a obtenir l’estructura tridimensional d’una proteïna.
- BRENDA. En tant que enzims, explorarem la seva funció i la seva classificació.
El primer que farem serà identificar quines són aquestes seqüències usant el programa BLAST a NCBI per a buscar les proteïnes per a les quals codifiquen (tinguem cura d’especificar que volem executar BLAST “contra” la base de dades Uniprot en el desplegable corresponent). Per exemple, en el cas de la proteîna del grup A obtenim un resultat a BLAST com el de la figura següent (mostrem només els 5 millors resultats):
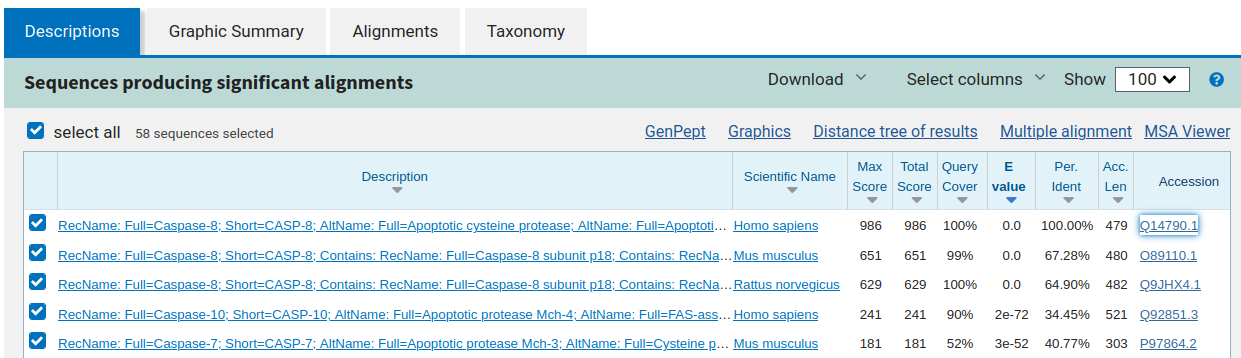
Accedint al codi d’accés Q14790.1de la drerta de la primera línea trobem que es tracta de la caspasa-8 humana, amb codi d’accés UNIPROT Q14790.
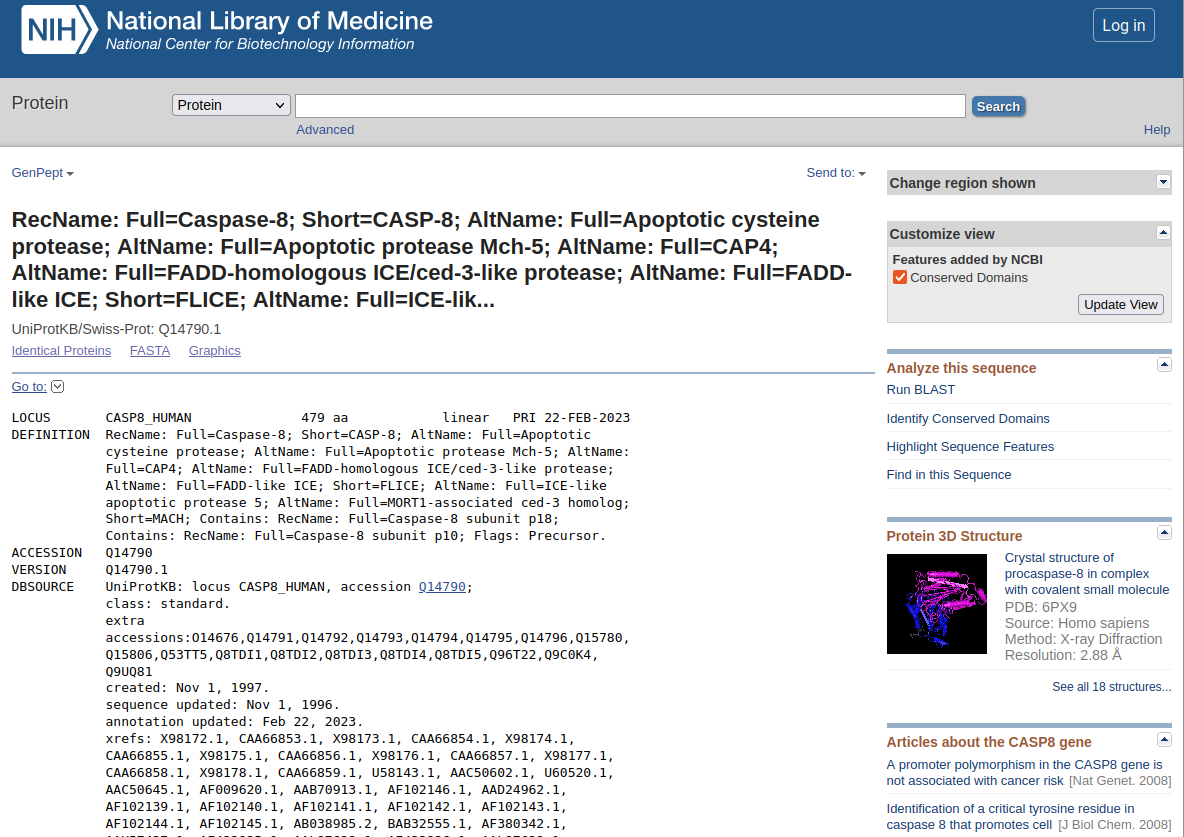
A la pròpia entrada UNIPROT hi trobem l’enllaç a BRENDA i el codi EC de l’enzim.
Així, identifiquem:
| Grup: proteïna | Codi UNIPROT | Codi BRENDA/ENZYME |
|---|---|---|
| A: Caspasa-8 | Q14790 | EC 3.4.22.61 |
| B: Kumamolisina | Q8RR56 | EC 3.4.21.B48 1 |
| C: Quimotripsina-C | Q99895 | EC 3.4.21.2 |
| D: BACE1 | P56817 | EC 3.4.23.46 |
| E: Taspasa 1 | Q9H6P5 | EC 3.4.25.1 2 |
| F: Carboxipeptidasa A1 | P15085 | EC 3.4.17.1 |
El més fàcil és accedir a la informació estructural directament des de la pàgina d’UNIPROT (secció Structure) sempre que estigui disponible (en general el més comú és no trobar estructures resoltes d’una proteïna al PDB i aleshores podem fer ús de la predicció que ens dona Alphafold2 accessible directament des de la pàgina d’UNIPROT). Fent-ho i escollint els PDB amb millor resolució i major cobertura, obtenim aquesta nova taula:
| Grup: proteïna [UNIPROT] | Funció 3 | Codi PDB i cadena |
|---|---|---|
| A: Caspasa-8 [Q14790] | Cisteina proteasa que juga un paper clau en la mort cel·lular programada actuant com a interruptor molecular per a l’apoptosi, la necroptosi i la piroptosi, i és necessària per prevenir danys en el teixit durant el desenvolupament embrionari i la vida adulta. | 1QTN_A |
| B: Kumamolisina [Q8RR56] | Serina proteasa, sedolisina hidrolitza preferentment pèptids que tenen un residu Ala o Pro a la posició P2 i prefereix residus d’aminoàcids carregats com Glu o Arg a la posició P2’.4 | 1T1E_A |
| C: Quimotripsina-C [Q99895] | Serina proteasa, Regula l’activació i la degradació de tripsinògens i procarboxipeptidases dirigint-se a llocs de tall específics dins dels seus zimogens. Té activitat proteasa de tipus quimotripsina i activitat hipocalcèmica. | 4H4F_A |
| D: BACE1 [P56817] | Aspartat proteasa Responsable del processament proteolític de la proteïna precursora de l’amiloide (APP). L’escissió a l’extrem N de la seqüència de pèptids A-beta, entre els residus 671 i 672 de l’APP, condueix a la generació i l’alliberament extracel·lular d’APP soluble escindida en beta, i un fragment C-terminal associat a la cèl·lula corresponent que s’allibera més tard. per gamma-secretasa | 1TQF_A |
| E: Taspasa 1 [Q9H6P5] | Treonina proteasa, responsable del processament i activació de KMT2A/MLL1. També activa KMT2D/MLL2 (Per similitud). Mitjançant l’activació del substrat, controla l’expressió dels gens HOXA i l’expressió de reguladors clau del cicle cel·lular, inclosos CCNA1, CCNB1, CCNE1 i CDKN2A (Per similitud) | 2A8J_A |
| F: Carboxipeptidasa A1 [P15085] | Metaloproteasa Carboxipeptidasa que catalitza l’alliberament d’un aminoàcid C-terminal, però té poca o cap acció amb -Asp, -Glu, -Arg, -Lys o -Pro | 5OM9_A |
| Grup: proteïna [UNIPROT] | Codi PDB i cadena / Domini | Visualització |
|---|---|---|
| A: Caspasa-8 [Q14790] | 1QTN_A SCOPe |
|
| B: Kumamolisina [Q8RR56] | 1T1E_A SCOPe |
|
| C: Quimotripsina-C [Q99895] | 4H4F_A SCOPe |
|
| D: BACE1 [P56817] | 1TQF_A SCOPe |
|
| E: Taspasa 1 [Q9H6P5] | 2A8J_A PFAM |
|
| F: Carboxipeptidasa A1 [P15085] | 5OM9_A SCOP |
|
Veure intro a estructures supersecundàries aquí.
© Jordi Villà Freixa, Facultat de Ciències, Tecnologia i Enginyeries, Universitat de Vic - Universitat Central de Catalunya, 2023
-
Cal notar que en aquest cas l’entrada UNIPROT no enllaça a BRENDA, però si entrem a BRENDA i cerquem directament el nom de la proteïna obtenim un preliminary BRENDA supplied EC number ↩
-
En aquest cas, en accedir a ENZYME des de la pàgina d’UNIPROT, obtenim dues opcions de codi, i hem agafat el primer. ↩
-
Si no s’especifica el contrari, la informació està extreta de la fitxa UNIPROT ↩
-
Informació obtinguda de la fitxa a BRENDA. ↩