QIEP
Flavin-containing monooxygenase 5
Grup A · Química i Enginyeria de Proteïnes 2024-2025
Seqüència problema
Aquesta és la cadena aminoacídica analitzada. La identificació de la proteïna o del constructe es fa a partir d’aquesta seqüència, i totes les correspondències amb UniProt, PDB, CATH/ECOD o AlphaFold s’han d’interpretar en relació amb aquesta numeració.
>sp|P49326|FMO5_HUMAN Flavin-containing monooxygenase 5 OS=Homo sapiens OX=9606 GN=FMO5 PE=1 SV=2 | 2024-2025 | seqüència problema
MTKKRIAVIGGGVSGLSSIKCCVEEGLEPVCFERTDDIGGLWRFQENPEEGRASIYKSVIINTSKEMMCFSDYPIPDHYP
NFMHNAQVLEYFRMYAKEFDLLKYIRFKTTVCSVKKQPDFATSGQWEVVTESEGKKEMNVFDGVMVCTGHHTNAHLPLES
FPGIEKFKGQYFHSRDYKNPEGFTGKRVIIIGIGNSGGDLAVEISQTAKQVFLSTRRGAWILNRVGDYGYPADVLFSSRL
THFIWKICGQSLANKYLEKKINQRFDHEMFGLKPKHRALSQHPTLNDDLPNRIISGLVKVKGNVKEFTETAAIFEDGSRE
DDIDAVIFATGYSFDFPFLEDSVKVVKNKISLYKKVFPPNLERPTLAIIGLIQPLGAIMPISELQGRWATQVFKGLKTLP
SQSEMMAEISKAQEEIDKRYVESQRHTIQGDYIDTMEELADLVGVRPNLLSLAFTDPKLALHLLLGPCTPIHYRVQGPGK
WDGARKAILTTDDRIRKPLMTRVVERSSSMTSTMTIGKFMLALAFFAIIIAYF
Seqüència recuperada de UniProt P49326. Longitud: 533 aminoàcids. Cisteïnes: 21, 22, 31, 69, 112, 147, 248, 468.
Identificació i estructura de referència
A partir de la seqüència anterior i de les bases de dades principals de seqüència i estructura, la proteïna s’identifica com a flavin-containing monooxygenase 5. L’estructura de treball s’ha d’interpretar sempre comprovant que el PDB triat cobreix prou bé la seqüència analitzada; si hi ha diversos PDB possibles, la resolució només és decisiva després de comprovar cobertura, identitat, estat del lligand i rellevància biològica.
| Camp | Valor |
|---|---|
| UniProt / gen | P49326; gen: FMO5 |
| EC / BRENDA | 1.14.13.8 |
| Estructura principal | 6SEK |
| Plegament o família | enzim flavoproteic amb FAD; plegament adaptat a transferència d’oxigen dependent de NADPH |
| Estructura secundària i lectura ChimeraX | domini flavoproteic mixt amb hèlixs i làmines que sostenen FAD i el lloc d’entrada de substrat; cal marcar ponts d’hidrogen interns i contactes al voltant del cofactor |
| Lligands, cofactors o lloc funcional | FAD/NADPH o anàlegs segons l’estructura triada; cal distingir cofactor i substrat xenobiòtic |
La transferència de residus funcionals requereix conservar la correspondència entre la numeració de la seqüència i la del model estructural, especialment quan l’estructura prové d’un homòleg, d’un domini aïllat o d’un model predictiu. FMO5 catalitza oxidacions dependents de FAD i NADPH, amb interès en metabolisme oxidatiu i especificitat de substrat.
Arquitectura molecular
FMO5 és una monooxigenasa dependent de FAD i NADPH. La lectura estructural se centra en el lloc d’unió de FAD, l’accés del NADPH i la cavitat on s’oxiden substrats orgànics.
Lloc funcional i mecanisme
El cicle catalític passa per reducció de FAD, activació d’oxigen i transferència d’un àtom d’oxigen al substrat. La geometria del cofactor i la xarxa de residus polars controlen la formació d’intermedis oxidants.
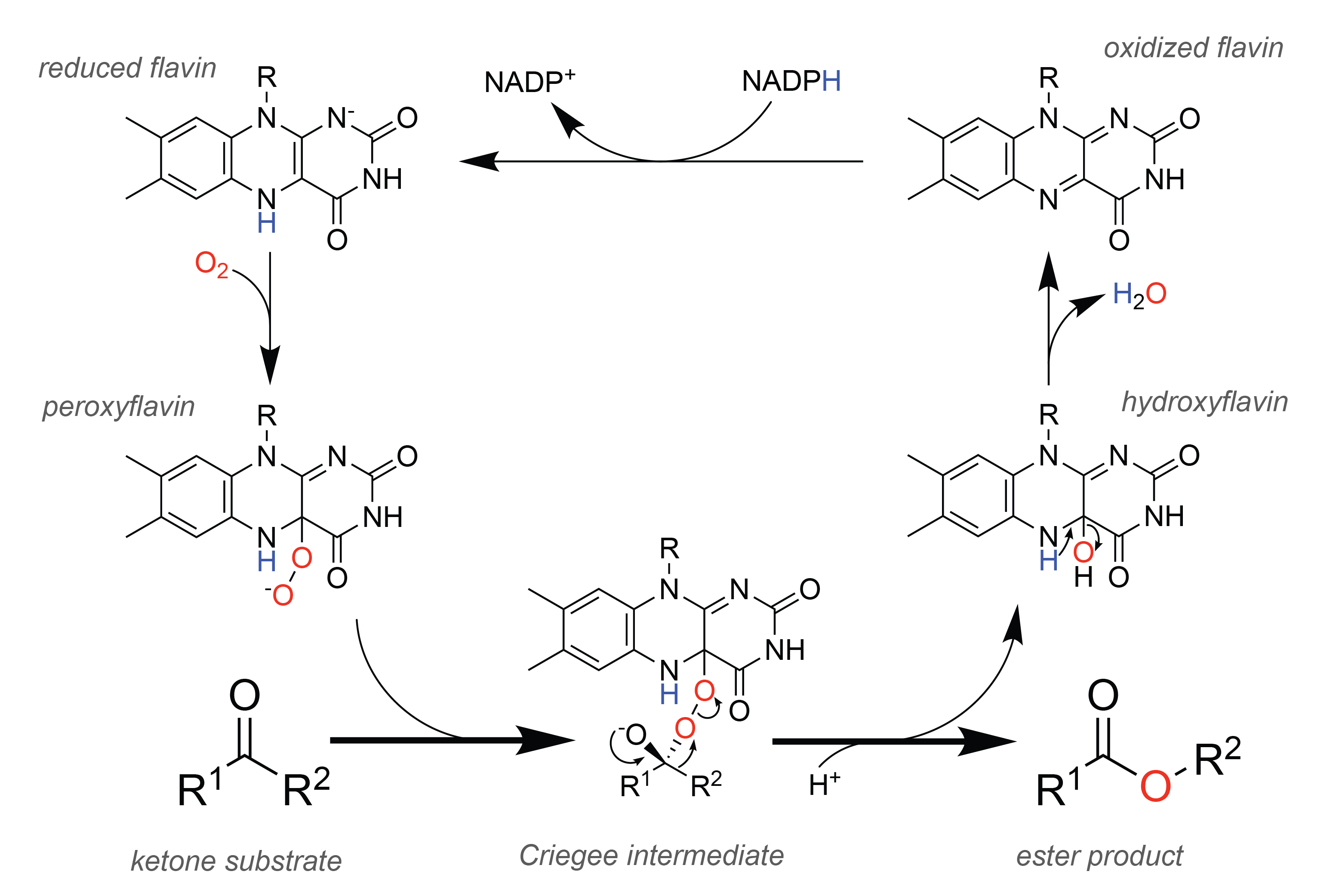
La interpretació estructural i funcional d’aquest sistema es pot situar en el context de la literatura experimental corresponent (Leisch et al., 2011).
Modificacions i variants
Les anotacions de variants i modificacions s’han de consultar a UniProt per FMO5 i traslladar-les només si el residu és present en la seqüència analitzada. Les modificacions, mutacions o variants només tenen valor estructural si s’indiquen amb residu, numeració i equivalència amb el PDB o model usat a les figures.
Relació seqüència-estructura-funció
La relació seqüència-estructura-funció s’ha d’interpretar situant sobre el model els residus que estabilitzen el plegament i els que defineixen el lloc funcional. Les variants, els lligands o els cofactors només són informatius si es manté la correspondència entre la numeració de la seqüència i la del PDB o model utilitzat.
Referències
- Leisch, H.; Morley, K.; Lau, P. C. K. (2011). Baeyer-Villiger Monooxygenases: More Than Just Green Chemistry. Chemical Reviews. doi: 10.1021/cr1003437.