QIEP
isomerasa de sacarosa
Grup E · Química i Enginyeria de Proteïnes 2024-2025
Seqüència problema
Aquesta és la cadena aminoacídica analitzada. La identificació de la proteïna o del constructe es fa a partir d’aquesta seqüència, i totes les correspondències amb UniProt, PDB, CATH/ECOD o AlphaFold s’han d’interpretar en relació amb aquesta numeració.
>tr|M1E1F7|M1E1F7_9HYPH Sucrose isomerase OS=Rhizobium sp. MX-45 OX=1071045 GN=mutB PE=1 SV=1 | 2024-2025 | seqüència problema
KPGAPWWKSAVFYQVYPRSFKDTNGDGIGDFKGLTEKLDYLKGLGIDAIWINPHYAspNTDNGYDISDYREVMKEYGTME
DFDRLMAELKKRGMRLMVDVVINHSSDQHEWFKSSRASKDNPYRDYYFWRDGKDGHEPNNYPSFFGGSAWEKDPVTGQYY
LHYFGRQQPDLNWDTPKLREELYAMLRFWLDKGVSGMRFDTVATYSKTPGFPDLTPEQMKNFAEAYTQGPNLHRYLQEMH
EKVFDHYDAVTAGEIFGAPLNQVPLFIDSRRKELDMAFTFDLICYDRALDRWHTIPRTLADFRQTIDKVDAIAGEYGWNT
FFLGNHDNPRAVSHFGDDRPQWREASAKALATVTLTQRGTPFIFQGDELGMTNYPFKTLQDFDDIEVKGFFQDYVETGKA
TAEELLTNVALTSRDNARTPFQWDDSANAGFTTGKPWLKVNPNYTEINAAREIGDPKSVYSFYRNLISIRHETPALSTGS
YRDIDPSNADVYAYTRSQDGETYLVVVNFKAEPRSFTLPDGMHIAETLIESSSPAAPAAGAASLELQPWQSGIYKVK
Seqüència recuperada de UniProt M1E1F7. Longitud: 557 aminoàcids. Cisteïnes: 284.
Identificació i estructura de referència
A partir de la seqüència anterior i de les bases de dades principals de seqüència i estructura, la proteïna s’identifica com a sacarosa isomerasa. L’estructura de treball s’ha d’interpretar sempre comprovant que el PDB triat cobreix prou bé la seqüència analitzada; si hi ha diversos PDB possibles, la resolució només és decisiva després de comprovar cobertura, identitat, estat del lligand i rellevància biològica.
| Camp | Valor |
|---|---|
| UniProt / gen | M1E1F7; gen: sucrose isomerase |
| EC / BRENDA | 5.4.99.11 |
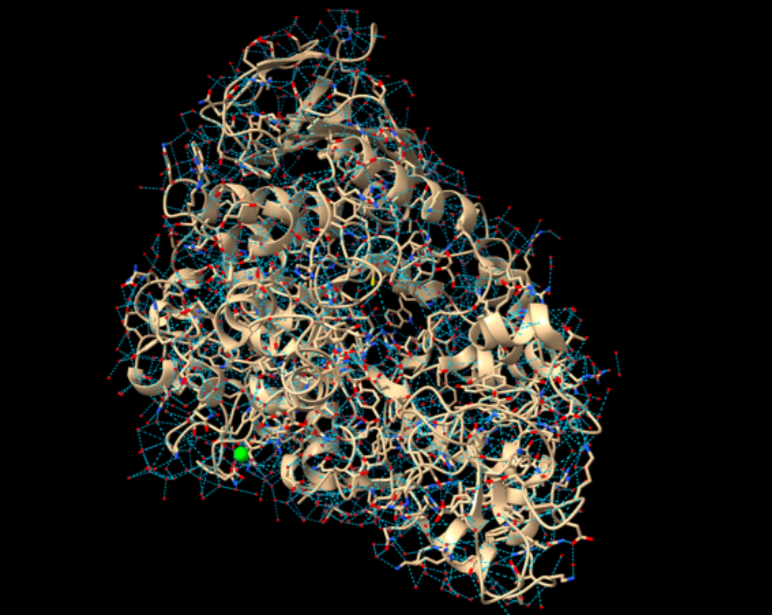
| Estructura principal | 4H2C |
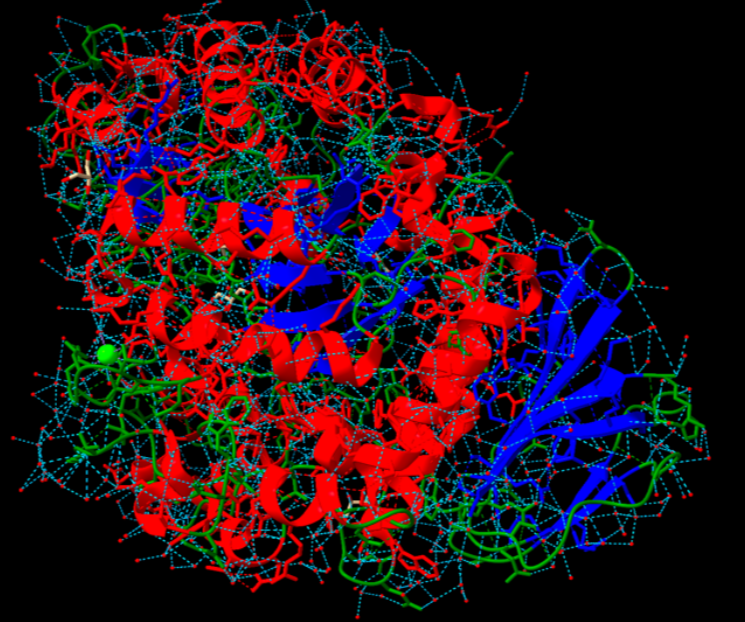
| Plegament o família | enzim de família GH13 amb barril catalític i dominis auxiliars de reconeixement de carbohidrats |
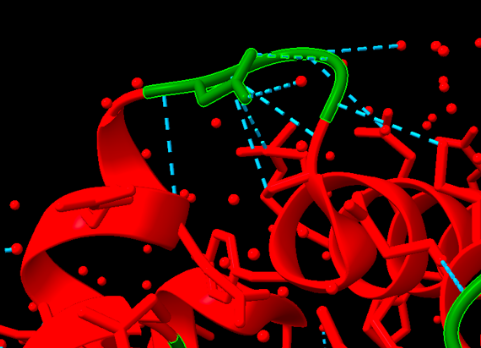
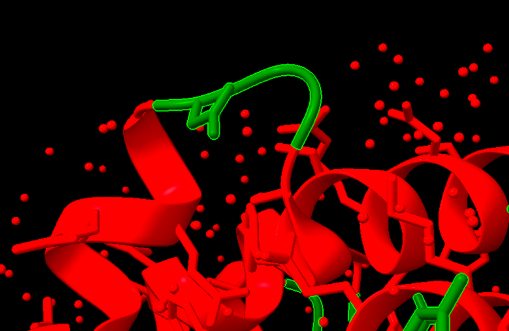
| Estructura secundària i lectura ChimeraX | barril catalític GH13 amb dominis auxiliars; el solc de carbohidrat i els residus àcids conservats defineixen la química |
| Lligands, cofactors o lloc funcional | sacarosa o inhibidors de carbohidrat al centre catalític; els residus àcids conservats executen la química glicosídica |
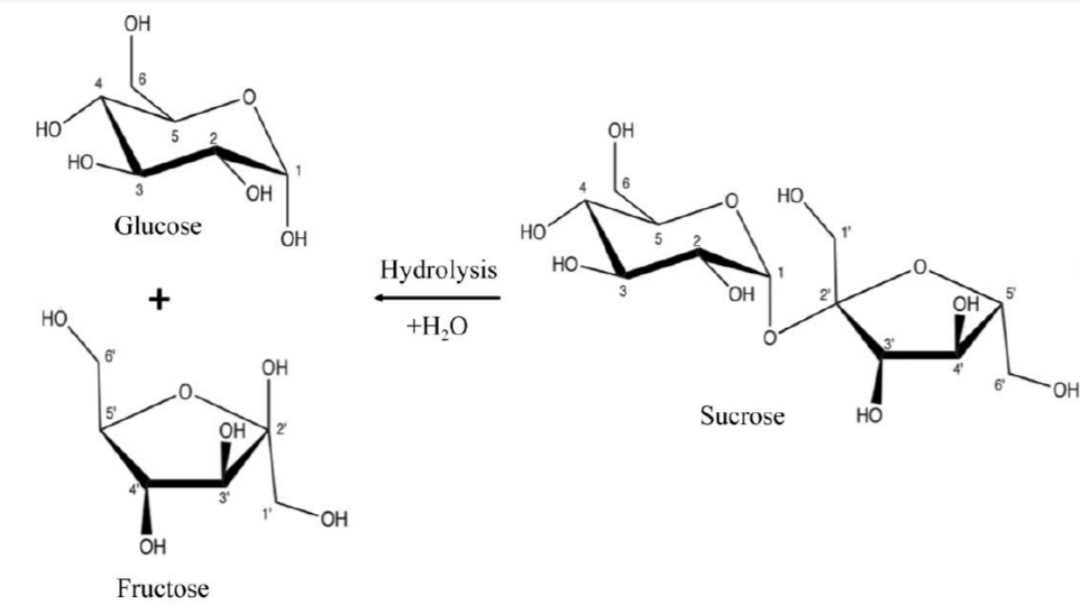
La transferència de residus funcionals requereix conservar la correspondència entre la numeració de la seqüència i la del model estructural, especialment quan l’estructura prové d’un homòleg, d’un domini aïllat o d’un model predictiu. La sucrosa isomerasa reordena l’enllaç glucosídic de la sucrosa i genera productes d’interès alimentari i biotecnològic.
Arquitectura molecular
La sucrosa isomerasa presenta un domini catalític de la família de glicosidases i una cavitat capaç de retenir els dos monosacàrids durant el reordenament de l’enllaç.
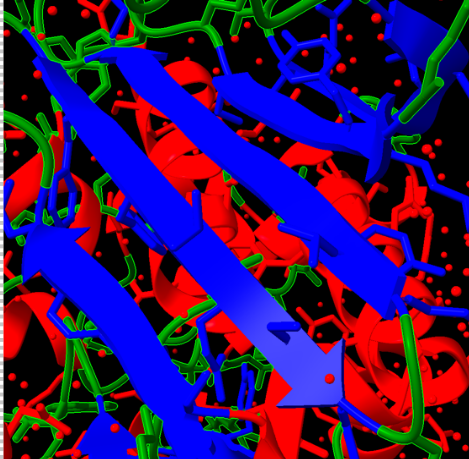
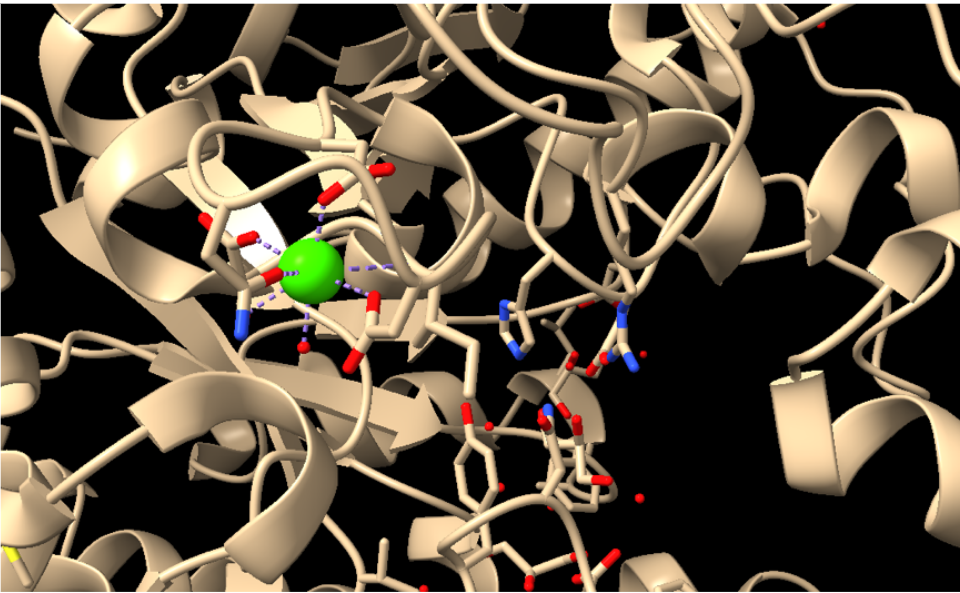
Lloc funcional i mecanisme
La reacció trenca i refà l’enllaç glucosídic sense una hidròlisi completa. La posició relativa de glucosa i fructosa determina la proporció d’isomaltulosa i altres productes.

La interpretació estructural i funcional d’aquest sistema es pot situar en el context de la literatura experimental corresponent (Ravaud et al., 2009).
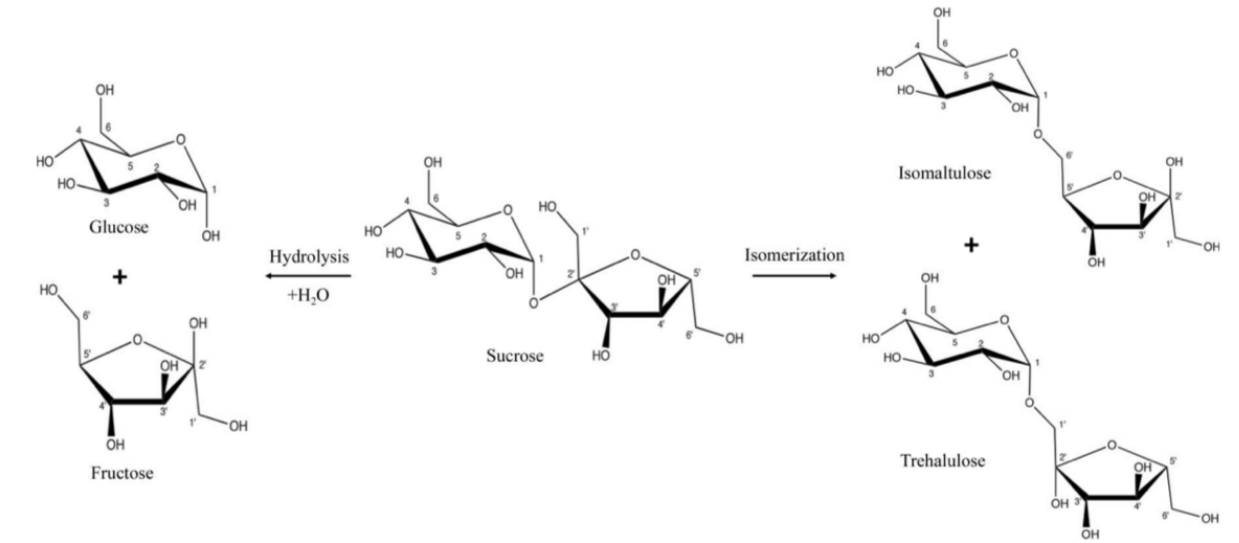
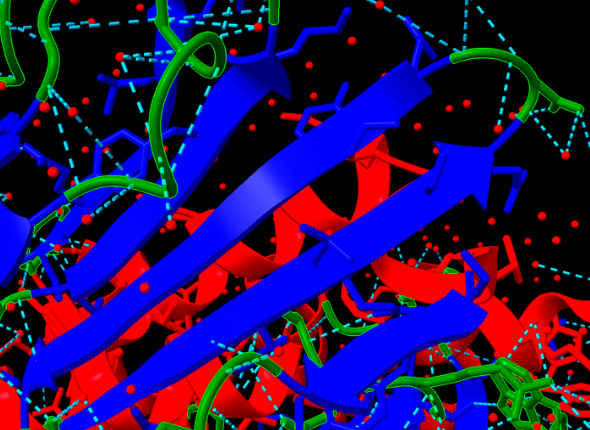
Modificacions i variants
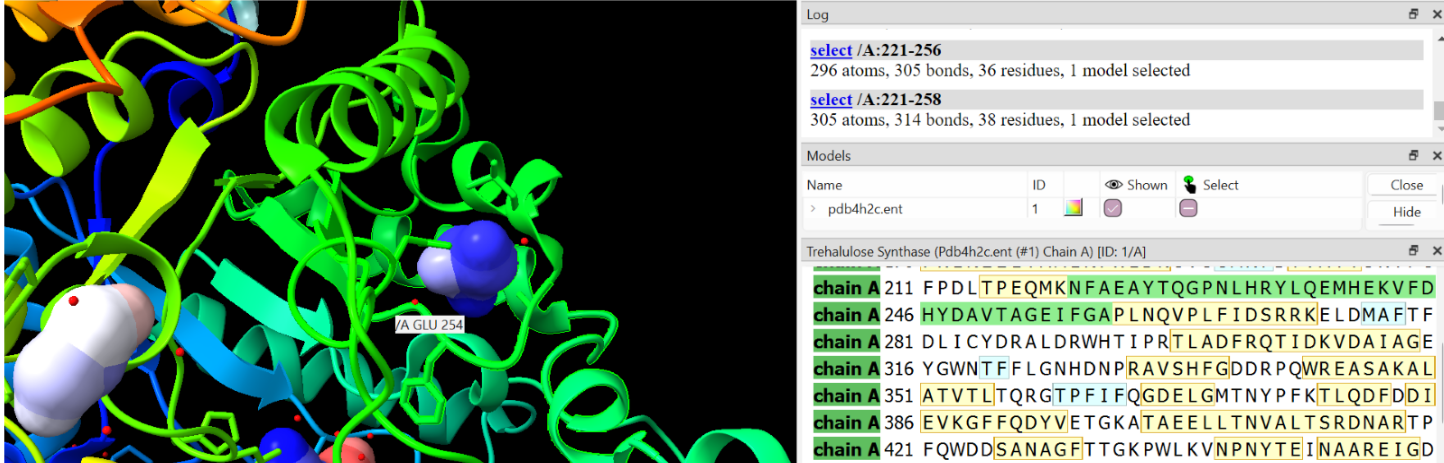
En el cas dels enzims bacterians/industrials el punt central és l’especificitat de producte i les mutacions de butxaca, més que modificacions posttraduccionals reguladores. Les modificacions, mutacions o variants només tenen valor estructural si s’indiquen amb residu, numeració i equivalència amb el PDB o model usat a les figures.
Relació seqüència-estructura-funció
La relació seqüència-estructura-funció s’ha d’interpretar situant sobre el model els residus que estabilitzen el plegament i els que defineixen el lloc funcional. Les variants, els lligands o els cofactors només són informatius si es manté la correspondència entre la numeració de la seqüència i la del PDB o model utilitzat.
Referències
- Ravaud, S. et al. (2009). Structural importants of product specificity of sucrose isomerases. FEBS Letters. doi: 10.1016/j.febslet. 2009.05.002.