QIEP
Lipasa
Grup M · Química i Enginyeria de Proteïnes 2024-2025
Seqüència problema
Aquesta és la cadena aminoacídica analitzada. La identificació de la proteïna o del constructe es fa a partir d’aquesta seqüència, i totes les correspondències amb UniProt, PDB, CATH/ECOD o AlphaFold s’han d’interpretar en relació amb aquesta numeració.
>sp|P41365|LIPB_PSEA2 Lipase B OS=Pseudozyma antarctica OX=84753 PE=1 SV=1 | 2024-2025 | seqüència problema
MKLLSLTGVAGVLATCVAATPLVKRLPSGSDPAFSQPKSVLDAGLTCQGAspSSVSKPILLVPGTGTTGPQSFDSNWIPL
STQLGYTPCWISPPPFMLNDTQVNTEYMVNAITALYAGSGNNKLPVLTWSQGGLVAQWGLTFFPSIRSKVDRLMAFAPDY
KGTVLAGPLDALAVSAPSVWQQTTGSALTTALRNAGGLTQIVPTTNLYSATDEIVQPQVSNSPLDSSYLFNGKNVQAQAV
CGPLFVIDHAGSLTSQFSYVVGRSALRSTTGQARSADYGITDCNPLPANDLTPEQKVAAAALLAPAAAAIVAGPKQNCEP
DLMPYARPFAVGKRTCSGIVTP
Seqüència recuperada de UniProt P41365. Longitud: 342 aminoàcids. Cisteïnes: 16, 47, 89, 241, 283, 318, 336.
Identificació i estructura de referència
A partir de la seqüència anterior i de les bases de dades principals de seqüència i estructura, la proteïna s’identifica com a lipasa. L’estructura de treball s’ha d’interpretar sempre comprovant que el PDB triat cobreix prou bé la seqüència analitzada; si hi ha diversos PDB possibles, la resolució només és decisiva després de comprovar cobertura, identitat, estat del lligand i rellevància biològica.
| Camp | Valor |
|---|---|
| UniProt / gen | segons lipasa analitzada; gen: lipase/triacylglycerol lipase |
| EC / BRENDA | 3.1.1.3 |
| Estructura principal | estructura del lliurament o homòleg experimental |
| Plegament o família | α/β hidrolasa amb triada Ser-His-Asp/Glu i sovint tapadora mòbil de la interfície |
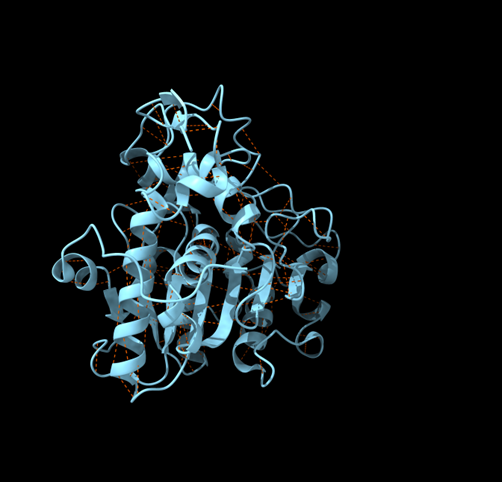
| Estructura secundària i lectura ChimeraX | α/β hidrolasa amb tapa mòbil; cal marcar triada catalítica, oxyanion hole i estat obert/tancat de la interfície lipídica |
| Lligands, cofactors o lloc funcional | substrat lipídic o inhibidor covalent; la catàlisi passa per acil-enzim i hidròlisi posterior |
La transferència de residus funcionals requereix conservar la correspondència entre la numeració de la seqüència i la del model estructural, especialment quan l’estructura prové d’un homòleg, d’un domini aïllat o d’un model predictiu. Les lipases hidrolitzen èsters lipídics i connecten catàlisi de serina amb reconeixement d’interfícies hidrofòbiques.
Arquitectura molecular
Les lipases presenten un nucli d’hidrolasa i superfícies hidrofòbiques adequades per treballar en interfícies oli-aigua. En molts casos, una tapa regula l’accés al centre actiu.
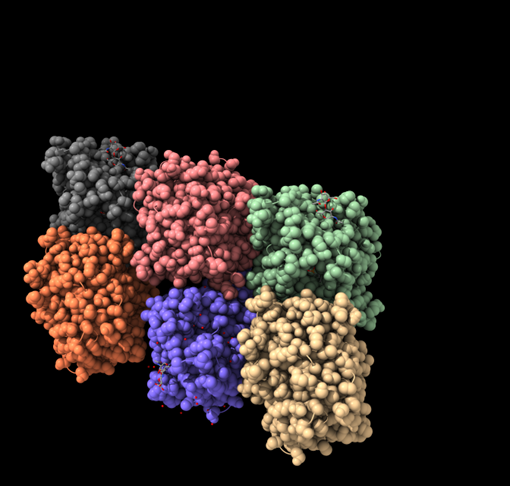
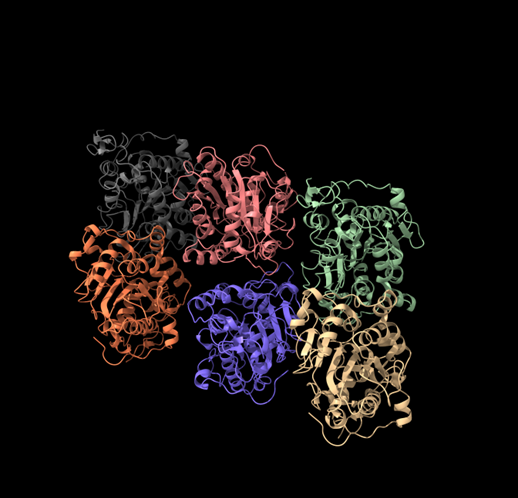
Lloc funcional i mecanisme
El mecanisme usa una serina nucleòfila, intermedi acil-enzim i hidròlisi final. L’activació interfacial connecta moviment estructural i accés del substrat lipídic.
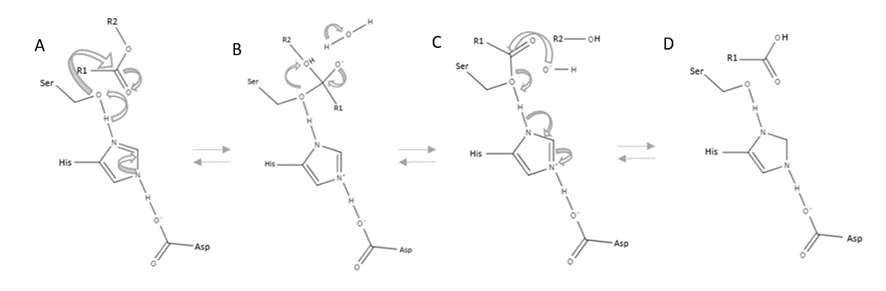
La interpretació estructural i funcional d’aquest sistema es pot situar en el context de la literatura experimental corresponent (Brzozowski et al., 1991).
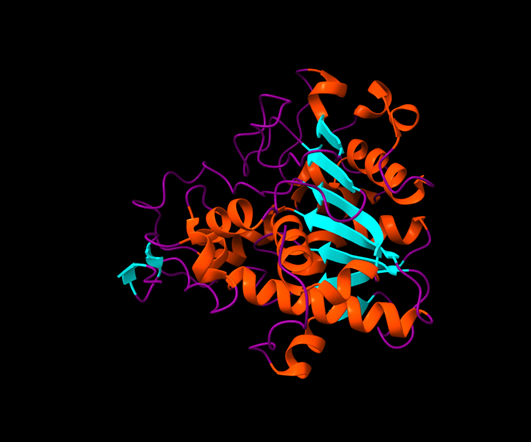
Modificacions i variants
En lipases secretades poden aparèixer ponts disulfur o glicosilació segons organisme; cal comprovar-los sobre la seqüència concreta. Les modificacions, mutacions o variants només tenen valor estructural si s’indiquen amb residu, numeració i equivalència amb el PDB o model usat a les figures.
Relació seqüència-estructura-funció
La relació seqüència-estructura-funció s’ha d’interpretar situant sobre el model els residus que estabilitzen el plegament i els que defineixen el lloc funcional. Les variants, els lligands o els cofactors només són informatius si es manté la correspondència entre la numeració de la seqüència i la del PDB o model utilitzat.


Referències
- Brzozowski, A. M. et al. (1991). A model for interfacial activation in lipases from the structure of a fungal lipase-inhibitor complex. Nature. doi: 10.1038/351491a0.